Armando el intrincado mapa de cómo se regulan los genes en una bacteria.
Heladia Salgado Osorio
¿Has pensado alguna vez en el mundo invisible que nos rodea, especialmente el de las bacterias? Aunque a veces nos causan cierto temor por relacionarlas con enfermedades, la realidad es que las bacterias son seres microscópicos esenciales para la vida, con su propio y fascinante universo, tan organizado y complejo como una ciudad bulliciosa. En cada gota de agua, en el suelo, en cada parte de nuestro cuerpo y en cada rincón del planeta, las bacterias llevan a cabo procesos clave, como ayudarnos a digerir alimentos o permitir el crecimiento de las plantas al fijar nitrógeno en el suelo. Estudiarlas nos revela cómo se adaptan y sobreviven en distintos ambientes.
Figura 1. Una gota de agua con bacterias, reflejando su presencia esencial en todos los rincones del planeta (generada con la asistencia de ChatGPT).
Dentro de la célula bacteriana se esconde un mundo en miniatura que funciona sin descanso. Los científicos han dedicado años en descifrar sus secretos. Identificaron los componentes básicos de la vida: los genes, que son las unidades de información que tienen las instrucciones para controlar cada actividad en la célula [1]. Estos genes son fragmentos escritos en el ADN, la molécula que actúa como un libro de instrucciones para el funcionamiento de la bacteria. Al leer la secuencia del ADN, descubrieron el código genético, un sistema de reglas que convierte o traduce la información del ADN en proteínas, esenciales para la vida. Pero una bacteria es más que su ADN: en su interior, moléculas y señales interactúan en un ecosistema dinámico, trabajando en conjunto como una ciudad en acción.
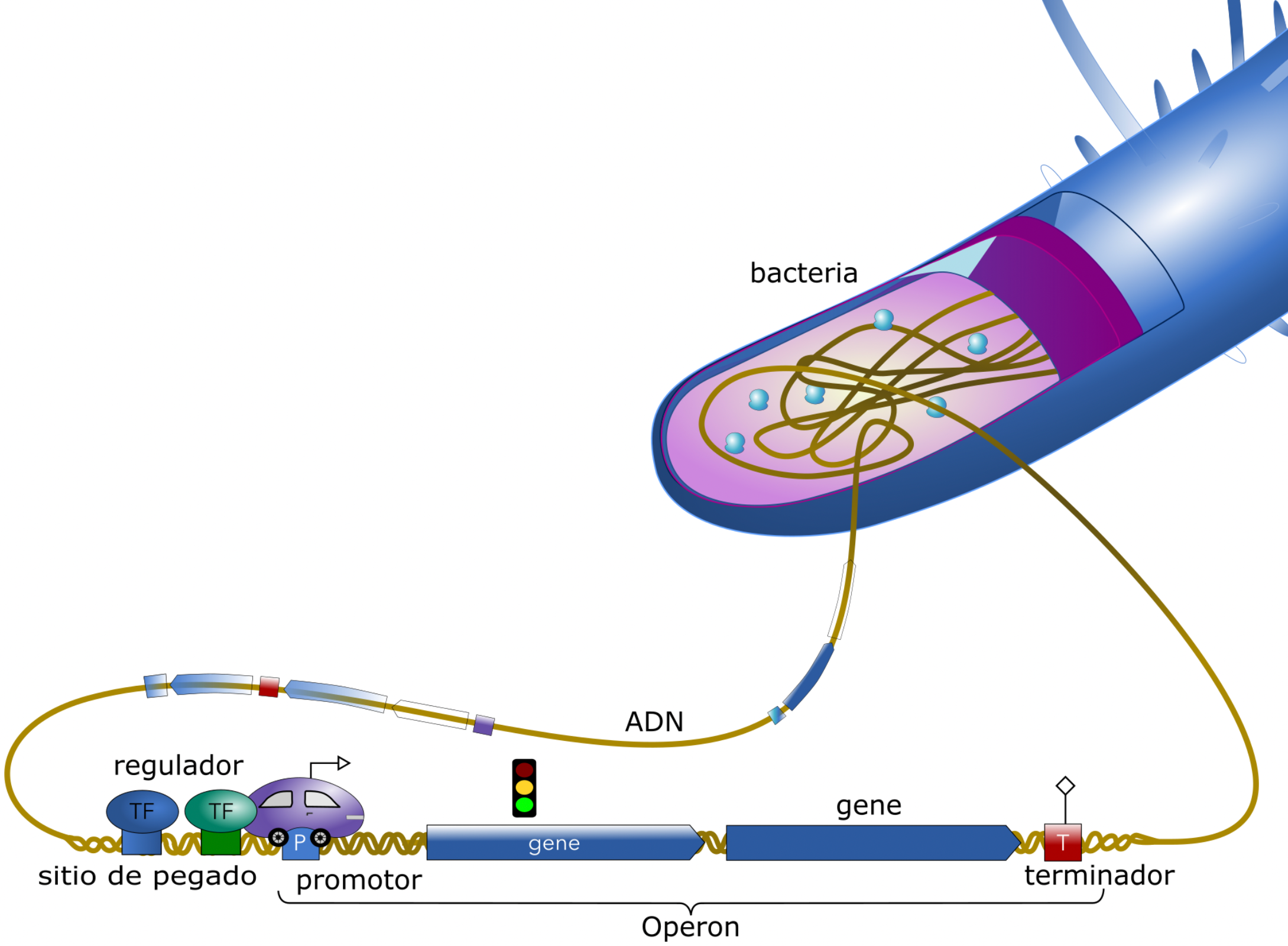
Figura 2. Imagen de Escherichia coli, una bacteria cuyo ADN contiene la información necesaria para su funcionamiento. En la ilustración se muestra cómo ciertos elementos del ADN ayudan a encender o apagar genes según las necesidades de la bacteria. (Imagen basada en el diseño original de Claire Rioualen, modificada bajo la licencia CC BY-NC-SA).
Imagina que esta pequeña ciudad regula el movimiento de moléculas y proteínas, como vehículos que siguen reglas para mantener el orden. En este "tráfico celular", los genes actúan como semáforos que pueden activar o desactivar funciones según sea necesario. Este proceso, llamado regulación, permite que la célula se adapte a distintos ambientes (Figura 2).
Descubrir cómo funciona esta ciudad microscópica nos permite explorar nuevas formas de entenderla y aplicarla en distintos campos. Aquí es donde entra en escena la bioinformática, que combina biología e informática para analizar los datos generados en el estudio de estos organismos. Con herramientas bioinformáticas, los científicos pueden descifrar secuencias genéticas, identificar patrones de regulación y construir modelos de cómo interactúan las moléculas dentro de la célula.
RegulonDB: Construyendo el rompecabezas de E. coli
Durante mi residencia profesional en 1994 en el Centro de Ciencias Genómicas de la UNAM, dentro del Programa de Genómica Computacional (PGC), tuve la oportunidad de adentrarme en la bioinformática bajo la guía del Dr. Julio Collado Vides. Fue en este espacio donde descubrí cómo las herramientas computacionales pueden ser clave para explorar, analizar y representar el conocimiento genético.
En ese momento, una de las principales líneas de investigación del laboratorio era la regulación de genes en Escherichia coli, impulsada por un estudio publicado en 1991 por el Dr. Collado [3]. Este trabajo recopiló y analizó información sobre promotores, pequeñas regiones del ADN que actúan como interruptores, y reguladores, moléculas que funcionan como agentes de tránsito, ambos coordinando el encendido y apagado de los genes (ver sección Operón en [1]). Así inició el arduo trabajo para organizar el conocimiento sobre la regulación genética en E. coli. Aunque en ese entonces los datos disponibles eran limitados, este esfuerzo permitió una mejor comprensión de esta compleja red biológica.
En este campo, investigar es como ser un "cazador de conocimiento", buscando, leyendo y ensamblando fragmentos de información para obtener una visión más completa de cómo funciona esta red genética. Pronto quedó claro que era necesario reunir en un solo lugar toda la información disponible sobre la regulación de E. coli, lo que dio origen a RegulonDB.
RegulonDB nació con el propósito de capturar, organizar y representar el conocimiento disperso en la literatura científica, facilitando su consulta para futuras investigaciones. En 1998, se publicó su primera versión, estructurando la información disponible hasta ese momento sobre la regulación genética en E. coli [4].
Siguiendo la analogía de una ciudad, además de los genes (semáforos), promotores (interruptores) y reguladores (agentes de tránsito), RegulonDB integró otros elementos esenciales del tráfico genético. El operón, comparable a una avenida con semáforos sincronizados, permite que un grupo de genes se active o desactive al mismo tiempo. Los sitios de unión, regiones de ADN a las que se unen proteínas reguladoras, funcionan como señales de tránsito, indicando a los reguladores dónde posicionarse para ejercer su control. El terminador, similar a un alto o el final de una calle, marca el punto donde la transcripción (el proceso mediante el cual la célula copia la información del ADN para producir proteínas) debe detenerse (Figura 3).
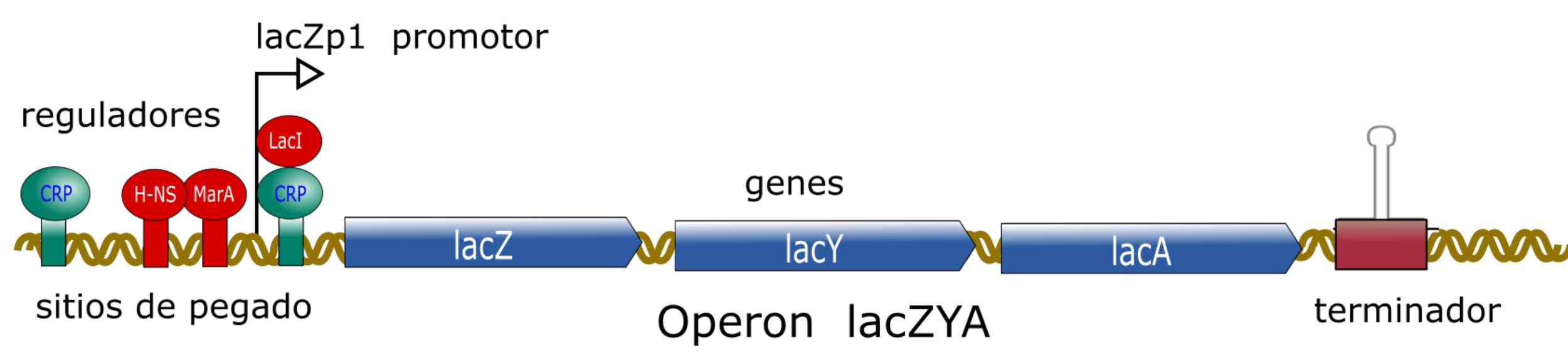
Figura 3. Una forma de hacer visible lo invisible: esta representación gráfica muestra cómo diferentes componentes de la célula trabajan en conjunto para regular el encendido y apagado de los genes. Se ilustra el operón llamado lac, un sistema que permite a E. coli activar genes cuando hay lactosa, un azúcar presente en la leche que la bacteria puede utilizar como fuente de energía. Se destacan los sitios de unión para los reguladores, el promotor, que inicia la transcripción y el terminador, que señala el final de la lectura de dicho operón.

Figura 4. La imagen resume el trabajo de años en RegulonDB, resultado de las contribuciones de muchos colaboradores, desde aquellos que se dedican a la extracción de conocimiento de los artículos científicos hasta el desarrollo e implementación de herramientas que facilitan la representación, exploración y análisis de datos sobre la regulación genética de E. coli.
Con el paso de los años, RegulonDB (https://regulondb.ccg.unam.mx/) se ha convertido en la base de datos primaria de la regulación transcripcional en Escherichia coli [5] (Figura 4). Hasta la fecha, tiene información de 14 mil 971 artículos científicos originales, cubriendo desde la revisión exhaustiva de 1991 realizada por el Dr. Collado hasta el presente (Salgado H). Además, las publicaciones periódicas de RegulonDB en la revista Nucleic Acids Research (NAR) han sido citadas en 2 mil 729 artículos de diversas áreas científicas (Scopus, noviembre 2024), y la base de datos ha registrado un promedio de 1,600 sesiones de usuario por mes en los últimos cuatro meses (según Google Analytics, ver Figura 5).
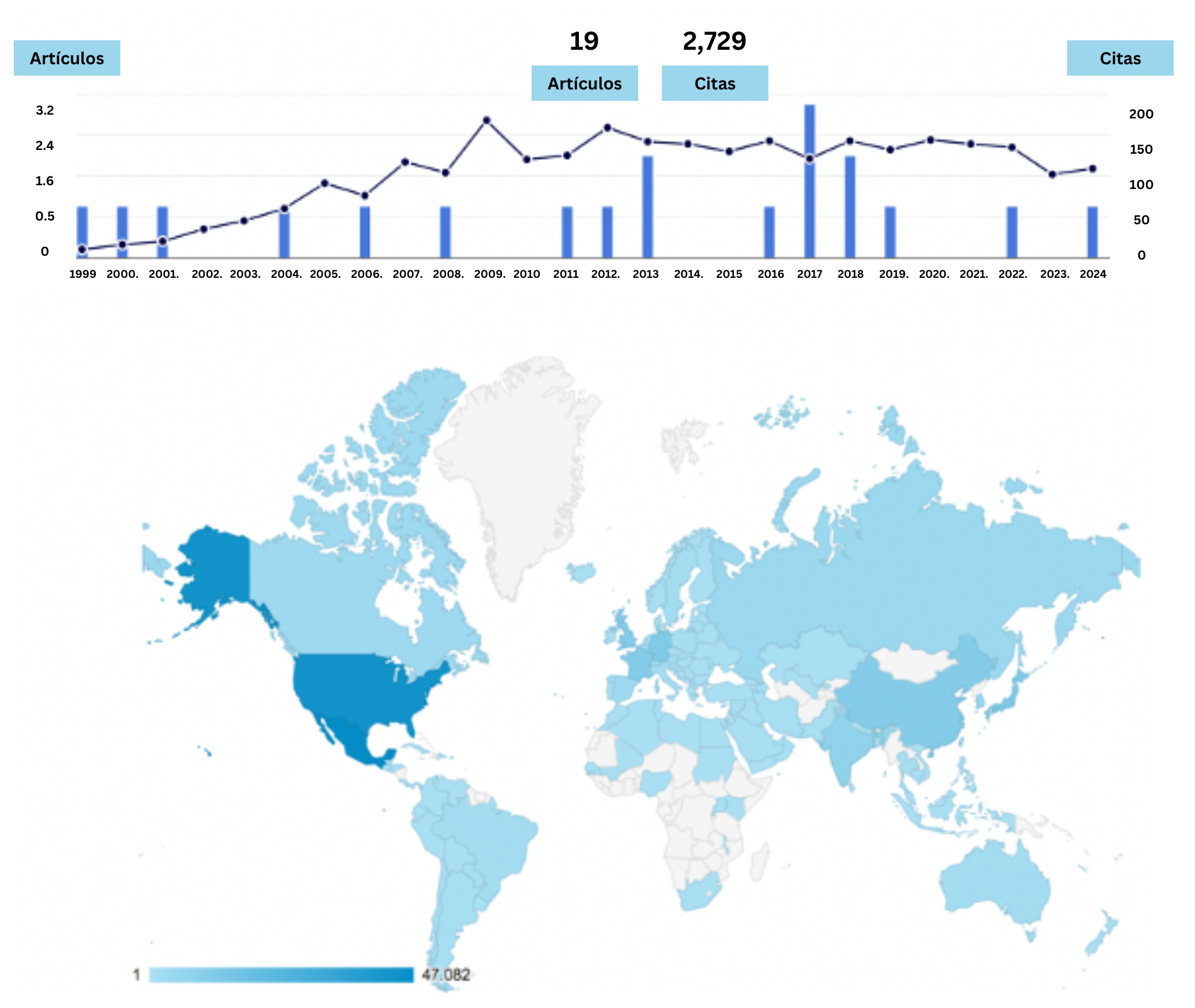
Figura 5. Representación del impacto de RegulonDB a lo largo del tiempo. En la parte superior, se muestra el número de artículos publicados (barras azules) y el número de citas recibidas por año (línea negra), destacando la relevancia sostenida de RegulonDB en la comunidad científica. En la parte inferior, el mapa mundial resalta un histórico de los países que han accedido a RegulonDB, mostrando su alcance global con mayor intensidad en regiones como América del Norte y Europa. La intensidad del color azul indica la frecuencia de acceso a la página web de RegulonDB.
Mi viaje con RegulonDB
Desde que me integré al PGC, he tenido el privilegio de ver nacer y evolucionar a RegulonDB, siendo parte activa de cada etapa de su desarrollo. Mi trabajo ha sido continuo, desde el mantenimiento de la infraestructura computacional que la sustenta hasta el diseño y desarrollo de software para analizar los datos que alberga. Siempre he sido una persona curiosa, con un profundo interés por aprender sobre cualquier tema que despierte mi atención. En el caso de la biología, me he dedicado a tomar cursos y leer literatura para entender mejor el área de investigación en la que colaboro. Este conocimiento no solo me ha permitido entender mejor cada concepto y herramienta que implementamos en RegulonDB, sino también actuar como un puente de interpretación entre el equipo técnico y los expertos en biología, facilitando la comunicación y asegurando que nuestras soluciones computacionales respondan a las necesidades reales de los proyectos.
A lo largo de los años, hemos mejorado continuamente el software de RegulonDB, asegurándonos de que sea más claro, eficiente y fácil de usar. Para ello, hemos adoptado buenas prácticas en su desarrollo y nos hemos capacitado en la creación de software de calidad. Además, seguimos estándares internacionales que permiten que la información en RegulonDB sea accesible, conectada con otros datos y reutilizable, facilitando su uso por la comunidad científica en todo el mundo.
RegulonDB ha sido no solo un espacio de desarrollo científico para nuestro grupo, sino también un motor de transformación personal y profesional. Cada avance técnico y científico refleja el esfuerzo continuo de un equipo colaborativo dedicado a construir un proyecto que hoy es un referente mundial en la regulación genética de E. coli.
Hoy, en un mundo donde la inteligencia artificial (IA) está revolucionando la manera en que generamos y analizamos conocimiento, RegulonDB también se encuentra en una nueva etapa de evolución. Las herramientas de la IA permitirán automatizar la búsqueda, extracción, integración y análisis de datos, facilitando el acceso a información que antes requería años de trabajo manual. Sin embargo, a pesar de estos avances, la ‘ciudad’ genética de E. coli aún tiene muchos secretos por revelar. No sabemos con certeza cómo evolucionará RegulonDB en el futuro, pero lo que sí es seguro es que el conocimiento seguirá expandiéndose, y nosotros seguiremos adaptándonos para explorarlo. La ciencia es un viaje en constante transformación, y con nuevas herramientas y mentes curiosas, estaremos mejor preparados para descifrar los secretos de esta fascinante 'ciudad' genética y de otros organismos que dan forma a la vida en nuestro planeta.
Referencias
- Checa Rojas, A. (2017). Gen: Desde el código genético hasta la ingeniería genética. Conogasi. Recuperado el 5 de marzo del 2025, de https://conogasi.org/articulos/gen-desde-el-codigo-genetico-hasta-la-ingenieria-genetica/
- Checa Rojas, A. (2017). ADN: Conceptos básicos y aplicaciones. Conogasi. Recuperado el 5 de marzo del 2025, de https://conogasi.org/articulos/adn-conceptos-basicos-y-aplicaciones/
- Collado-Vides, J., Magasanik, B., & Gralla, J. D. (1991). Control site location and transcriptional regulation in Escherichia coli. Microbiological Reviews, 55(3), 371–394. DOI: 10.1128/mr.55.3.371-394.1991.
- Huerta, A. M., Salgado, H., Thieffry, D., & Collado-Vides, J. (1998). RegulonDB: A database on transcriptional regulation in Escherichia coli. Nucleic Acids Research, 26(1), 55–59. DOI: 10.1093/nar/26.1.55
- Salgado, H., Gama-Castro, S., Lara, P., Mejia-Almonte, C., Alarcon-Carranza, G., López-Amazo, A. G., Betancourt-Figueroa, F., Peña-Loredo, P., Alquicira, C., Hernández, S., Ledezma-Tejeida, D., et al. (2024). RegulonDB v12.0: A comprehensive resource for transcriptional regulation in E. coli K-12. Nucleic Acids Research, 52, D255-D264. DOI: 10.1093/nar/gkad1072.
Lecturas recomendadas
- Checa Rojas, A. (2017). Gen: Desde el código genético hasta la ingeniería genética. Conogasi. Recuperado el 5 de marzo del 2025, de https://conogasi.org/articulos/gen-desde-el-codigo-genetico-hasta-la-ingenieria-genetica/
- Checa Rojas, A. (2017). ADN: Conceptos básicos y aplicaciones. Conogasi. Recuperado el 5 de marzo del 2025, de https://conogasi.org/articulos/adn-conceptos-basicos-y-aplicaciones/
- Wikipedia contributors. (Última actualización: 2024). Regulación génica en procariotas. Wikipedia, La Enciclopedia Libre. Recuperado el 5 marzo de 2025, de https://es.wikipedia.org/wiki/Regulacióng%C3%A9nicaen_procariotas
Comparte este artículo en redes sociales

Acerca de los autores
Heladia Salgado es una académica en el área de bioinformática, siempre impulsada por su curiosidad y ganas de aprender. Su trayectoria la ha llevado de la computación a la biología, donde ha contribuido al desarrollo de RegulonDB, una base de datos clave en el estudio de la regulación genética. Además de su labor en investigación, ha formado a numerosas generaciones de estudiantes en bioinformática, compartiendo su conocimiento y promoviendo el uso de herramientas computacionales para el análisis genómico. Para Heladia, la ciencia es un viaje sin fin, donde siempre hay mucho que hacer y descubrir, donde cada respuesta abre la puerta a nuevas preguntas. Actualmente forma parte del Programa de Genómica Computacional del Centro de Ciencias Genómicas de la Universidad Nacional Autónoma de México.
Contacto: heladia@ccg.unam.mx

